Как я могу сделать триплет cca, используя scikit-bio (python)?
Как я могу сделать триплот для CCA, используя scikit-bio (python)?
Я пытаюсь сделать триплет из анализа канонической корреспонденции; например: 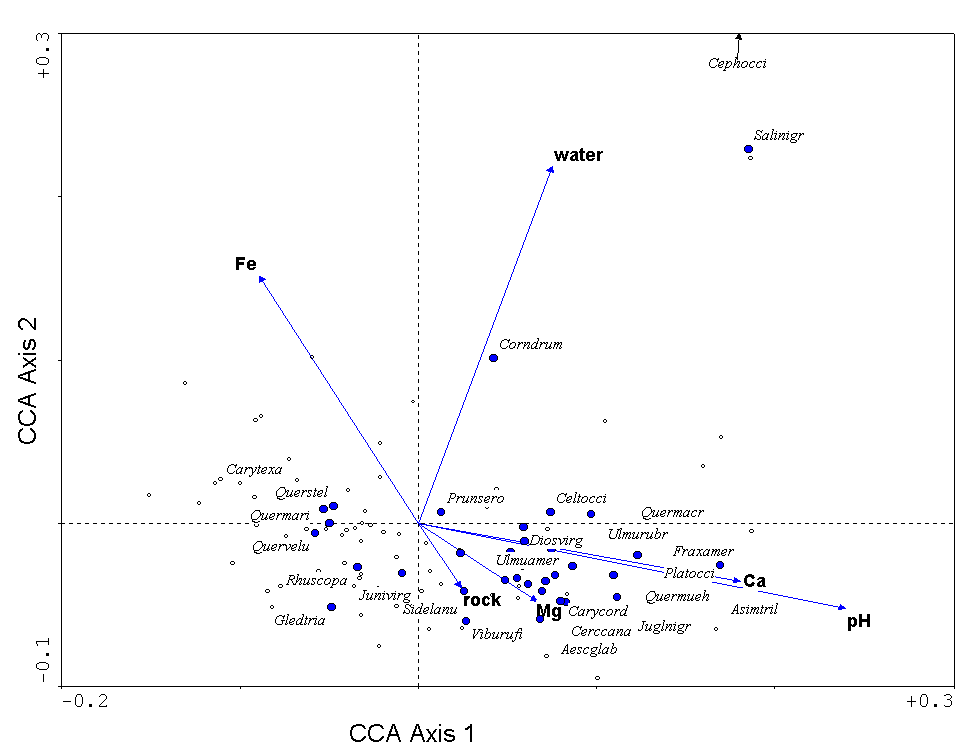
Это должно иметь точки как для образцов, так и для видов, а также иметь векторы для переменных среды. Визуализация по умолчанию, предоставляемая skbio это 3D-сюжет. Я могу сделать двухмерный график образцов и видов из данных, но я не могу понять, как получить информацию для векторов переменных среды.
import numpy as np
import pandas as pd
import matplotlib.pyplot as plt
import skbio
# I'll use the sample data from the skbio website
# http://scikit-bio.org/docs/latest/generated/skbio.stats.ordination.html#module-skbio.stats.ordination
X = np.array([[1.0, 0.0, 1.0, 0.0],
[2.0, 0.0, 1.0, 0.0],
[3.0, 0.0, 1.0, 0.0],
[4.0, 0.0, 0.0, 1.0],
[5.0, 1.0, 0.0, 0.0],
[6.0, 0.0, 0.0, 1.0],
[7.0, 1.0, 0.0, 0.0],
[8.0, 0.0, 0.0, 1.0],
[9.0, 1.0, 0.0, 0.0],
[10.0, 0.0, 0.0, 1.0]])
transects = ['depth', 'substrate_coral', 'substrate_sand',
'substrate_other']
sites = ['site1', 'site2', 'site3', 'site4', 'site5', 'site6', 'site7',
'site8', 'site9', 'site10']
X = pd.DataFrame(X, sites, transects)
del X['substrate_other']
species = ['specie1', 'specie2', 'specie3', 'specie4', 'specie5',
'specie6', 'specie7', 'specie8', 'specie9']
Y = np.array([[1, 0, 0, 0, 0, 0, 2, 4, 4],
[0, 0, 0, 0, 0, 0, 5, 6, 1],
[0, 1, 0, 0, 0, 0, 0, 2, 3],
[11, 4, 0, 0, 8, 1, 6, 2, 0],
[11, 5, 17, 7, 0, 0, 6, 6, 2],
[9, 6, 0, 0, 6, 2, 10, 1, 4],
[9, 7, 13, 10, 0, 0, 4, 5, 4],
[7, 8, 0, 0, 4, 3, 6, 6, 4],
[7, 9, 10, 13, 0, 0, 6, 2, 0],
[5, 10, 0, 0, 2, 4, 0, 1, 3]])
Y = pd.DataFrame(Y, sites, species)
# End sample data
# Perform CCA on the sample data
cca_test = skbio.stats.ordination.cca(y=Y, x=X)
# 2d plot of samples and species
plt.scatter(x=cca_test.samples['CCA1'], y=cca_test.samples['CCA2'], color='blue')
plt.scatter(x=cca_test.features['CCA1'], y=cca_test.features['CCA2'], color='red')
# Where are the environment variables?