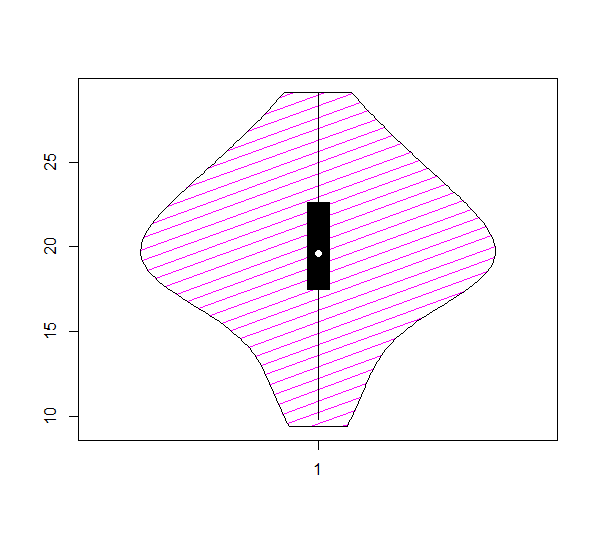
Узор заливки скрипичных участков (пакет виоплота)
Есть ли способ заполнять участки скрипки разными узорами при использовании vioplot пакет для создания сюжетов в R?
Я понял, как изменить цвет, используя col, как показано ниже. Но я даже не знаю, как начать со штриховки в виоплоте.
vioplot(random_value, at = 0.5, add = T, h = 0.04, col = 'lightsalmon4')
я использовал density а также angle но это не помогает
1 ответ
Решение
Я отвечаю на свой вопрос только на тот случай, если он будет полезен кому-то еще позже. Это похоже на vioplot Сам пакет не допускает "штриховку" или "текстуру" на скрипке, которую он создает. Тем не менее, кажется, что это может быть достигнуто путем внесения небольших изменений по умолчанию vioplot функция для включения density а также angle к многоугольнику это создает как участки скрипки.
vioplot2 = function (x, ..., range = 1.5, h = NULL, ylim = NULL, names = NULL,
horizontal = FALSE, col = "magenta", border = "black", lty = 1,
lwd = 1, rectCol = "black", density = NA, angle = 45, colMed = "white", pchMed = 19,
at, add = FALSE, wex = 1, drawRect = TRUE)
{
datas <- list(x, ...)
n <- length(datas)
if (missing(at))
at <- 1:n
upper <- vector(mode = "numeric", length = n)
lower <- vector(mode = "numeric", length = n)
q1 <- vector(mode = "numeric", length = n)
q3 <- vector(mode = "numeric", length = n)
med <- vector(mode = "numeric", length = n)
base <- vector(mode = "list", length = n)
height <- vector(mode = "list", length = n)
baserange <- c(Inf, -Inf)
args <- list(display = "none")
if (!(is.null(h)))
args <- c(args, h = h)
for (i in 1:n) {
data <- datas[[i]]
data.min <- min(data)
data.max <- max(data)
q1[i] <- quantile(data, 0.25)
q3[i] <- quantile(data, 0.75)
med[i] <- median(data)
iqd <- q3[i] - q1[i]
upper[i] <- min(q3[i] + range * iqd, data.max)
lower[i] <- max(q1[i] - range * iqd, data.min)
est.xlim <- c(min(lower[i], data.min), max(upper[i],
data.max))
smout <- do.call("sm.density", c(list(data, xlim = est.xlim),
args))
hscale <- 0.4/max(smout$estimate) * wex
base[[i]] <- smout$eval.points
height[[i]] <- smout$estimate * hscale
t <- range(base[[i]])
baserange[1] <- min(baserange[1], t[1])
baserange[2] <- max(baserange[2], t[2])
}
if (!add) {
xlim <- if (n == 1)
at + c(-0.5, 0.5)
else range(at) + min(diff(at))/2 * c(-1, 1)
if (is.null(ylim)) {
ylim <- baserange
}
}
if (is.null(names)) {
label <- 1:n
}
else {
label <- names
}
boxwidth <- 0.05 * wex
if (!add)
plot.new()
if (!horizontal) {
if (!add) {
plot.window(xlim = xlim, ylim = ylim)
axis(2)
axis(1, at = at, label = label)
}
box()
for (i in 1:n) {
polygon(c(at[i] - height[[i]], rev(at[i] + height[[i]])),
c(base[[i]], rev(base[[i]])), col = col, density = density, angle = angle, border = border,
lty = lty, lwd = lwd)
if (drawRect) {
lines(at[c(i, i)], c(lower[i], upper[i]), lwd = lwd,
lty = lty)
rect(at[i] - boxwidth/2, q1[i], at[i] + boxwidth/2,
q3[i], col = rectCol)
points(at[i], med[i], pch = pchMed, col = colMed)
}
}
}
else {
if (!add) {
plot.window(xlim = ylim, ylim = xlim)
axis(1)
axis(2, at = at, label = label)
}
box()
for (i in 1:n) {
polygon(c(base[[i]], rev(base[[i]])), c(at[i] - height[[i]],
rev(at[i] + height[[i]])), col = col, density = density, angle = angle, border = border,
lty = lty, lwd = lwd)
if (drawRect) {
lines(c(lower[i], upper[i]), at[c(i, i)], lwd = lwd,
lty = lty)
rect(q1[i], at[i] - boxwidth/2, q3[i], at[i] +
boxwidth/2, col = rectCol)
points(med[i], at[i], pch = pchMed, col = colMed)
}
}
}
invisible(list(upper = upper, lower = lower, median = med,
q1 = q1, q3 = q3))
}
ИСПОЛЬЗОВАНИЕ
set.seed(42)
x = rnorm(50,20,4)
vioplot2(x,density = 9, angle = 20)